(Updated on 2013/8/4)
理化学研究所脳科学総合研究センター
チームリーダー Markus Diesmann
単純な神経細胞モデルから出発し、実際の脳の活動が説明できるのか否かを解明する
Point-neuron model
ハイブリッドODE+point-event solver
ハイブリッド(MPI+スレッド) at same granularity
C++, SLI, MPI, pthread
公開済み。ソース・コードをISLiMダウンロードサイト経由で入手可能。
京コンピューターの全計算ノード82,944個(約70万個のCPUコア)を使用した、17億3,000万個の神経細胞が10兆4,000億個のシナプスで結合された神経回路のシミュレーション (2013.8.2)。
最大64万コア並列以上
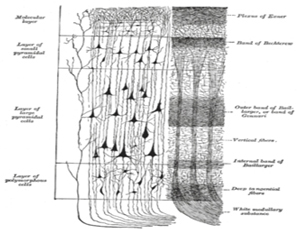
大脳皮質の情報処理単位1コラム(1 mm2)
- 大脳皮質の10,000コラム以上に相当する17億神経細胞、および神経細胞間を接続するシナプス10兆個の信号処理を再現・予測できるようになる
- 京計算機を用いて数十万並列の実行が実現可能となる。世界最速を目指す。
理化学研究所脳科学総合研究センター
チームリーダー 深井朋樹
6層構造を持つ皮質局所回路がどのようにして情報処理を実現しているかを、生理実験データに基づく大規模シミュレーションによって明らかにする。
コンダクタンスベースの神経細胞モデル
連立非線形微分方程式の数値解析による求解
ハイブリットMPIとスレッド並列による神経細胞とシナプスの均一粒度分割
C++, SLI, MPI, GSL
公開予定
- RICCを用いて256並列実行
- メモリ容量 約25GB、ディスク容量 200MB
- 10万コア並列
- メモリ容量 2.5TB 、ディスク容量 20 TB
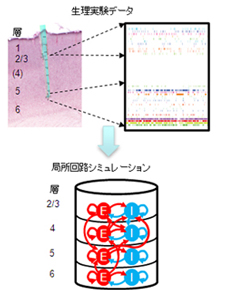
- 皮質の各層の神経細胞同士で起きる複雑な相互作用が、情報処理機構をどのように実現しているかの手掛かりを得られる。
- 脳の情報処理機構を理解することで、超低消費電力で柔軟な処理を行う脳型情報処理技術実現の手掛かりを得られる。
理化学研究所脳科学総合研究センター
チームリーダー 臼井支朗
計算対象は、機能、細胞、イオン電流の各レベルで記述された眼球運動(脳幹)、眼光学、網膜、皮質の数理モデルで構成された視覚系、また、共有フォーマットによるモデル統合ならびにシミュレーションライブラリ
イオン電流、またはコンダクタンスベースの細胞モデル、畳み込み演算による受容野や網膜像
Runge-Kutta法、畳み込み演算
空間分割
C, C++, OpenMPI, GSL, netCDF
ISLiMダウンロードサイトから公開済み
眼球運動(特に微小眼球運動)の生成メカニズム、詳細な網膜像ならびに視細胞出力の生成、皮質における動き検出のメカニズムをRICCの数十コアで解析
全視覚系大規模モデルによる錯視シミュレーションを1000コアで解析
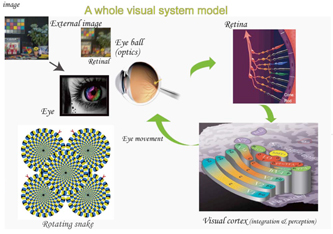
全視覚系モデルの概念図
- 視覚系を構成する各数理モデルを詳細化することで、薬品が視覚機能(例えば色覚など)に及ぼす副作用の評価・試験に役立つものと考えられる。
- 全視覚系を構成した数理モデルによるシミュレーションでは、視覚系の各部位における情報処理の可視化や計算科学的な立場からの視覚機能 (例えば錯視のメカニズム)の解析に役立つものと考えられる。
京都大学大学院情報学研究科 行縄直人
神経細胞におけるマルチフィジックス(骨格系、細胞膜、細胞内分子の反応拡散)を統合的にシミュレーションするためのソフトウェアプラットフォーム。
マルチコンパートメント反応拡散、細胞膜の離散化
Runge-Kutta法、最急降下法
膜エネルギー最適化およびアクチンキネティクス計算のOpenMP, MPIによるハイブリッド並列化。
C, C++, MPI, OpenMP, GSL, NetCDF, GD, zlib
ISLiMダウンロードサイトから公開済み
- モデル細胞の形態変化シミュレーション
- 128,000アクチン、50膜ノード、100x100ボクセル
- 64コア使用、メモリ容量 200 MB、ディスク容量 100 MB
- 神経形態形成にかかわる運動性のシミュレーション
- 100万アクチン、2,000膜ノード、128x128x128ボクセル
- メモリ容量 4 TB 、ディスク容量 2 TB
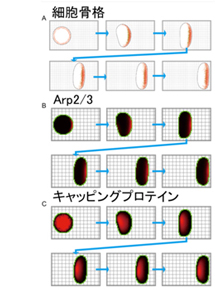
細胞骨格系分子反応と膜骨格系の動力学を考慮した細胞移動のシミュレーション
- 軸索伸長などの細胞移動のリアルタイムにせまるシミュレーションが可能となる。
- 骨格制御に関わる各分子が形態変化に対しどのような影響を与えているかを定量的に検証できる。
東京大学先端科学技術研究センター教授 神崎亮平
昆虫の感覚から行動までの神経回路の情報処理を、個々の神経形態を考慮したマルチコンパートメントモデルを用いて仮想3次元空間内でリアルタイムシミュレーションを行う。
コンダクタンスベース・マルチコンパートメントモデル
後退オイラー法、クランク・ニコルソン法、適応積分法
細胞ごとのプロセス分割(1細胞の分割も可能)
C, C++, MPI, SUNDAIL InterView
公開済み。ソース・コードをISLiMダウンロードサイト経由で入手可能。
- LALの神経回路シミュレーション
- 1024細胞を1024コアで解析
- メモリ容量 1TB、ディスク容量 10 GB
- 昆虫の嗅覚系の感覚から行動までの神経回路の情報処理のシミュレーションをリアルタイム以上で計算する
- 1万ニューロン・5千万コンパートメントを30万コアで解析
- メモリ容量 100 TB 、ディスク容量 1 TB
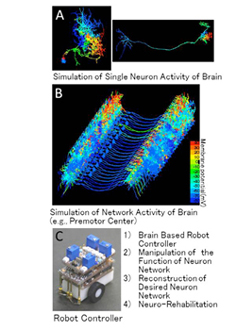
昆虫(カイコガ)の脳神経活動のシミュレーションの例
- 感覚から出力までの神経回路の情報処理が理解できるようになる
- 昆虫の一部の神経に与える変異が情報処理に与える影響が判る。
- ニューロリハビリテーションやニューロ・エンハンスメントの設計論の手がかりが得られる。